杭州地區相同分子型別的單核細胞增生李斯特菌臨床和食品分離株基因組分析
俞 驊,董華麗,汪皓秋,樓秀芹,劉 濤,張 蔚,王旭初,潘勁草
單核細胞增生李斯特菌(Listeriamonocytogenes)是一種常見的食源性致病菌,在肉、蔬菜、水果、冷凍飲品等食品中均能檢出,可引起人畜疾病。免疫力低下者攝入該菌會引起李斯特菌病,癥狀主要為腦膜炎、敗血癥和流產等,嚴重的可以造成死亡。李斯特菌病平均潛伏期為2~3周,最長可超過70 d[1-2]。一旦發病,特別是散發病例,進行食物來源溯源非常困難。近年來在歐美發達國家造成多起由其引起的食物中毒嚴重暴發事件,死亡率甚至可達20%~30%[3]。而在國內散發病例(如造成孕產婦流產)較為常見[4]。
引起李斯特菌病的血清型主要是1/2a、1/2b和4b,分子分型和溯源一般采用脈沖場凝膠電泳(Pulse-field gel electrophoresis,PFGE)。但傳統的分子分型方法受限于分析位點限制,分辨力有限。隨著高通量測序和生物信息學技術的快速發展,基于細菌核心基因組或全基因組SNPs位點進行溯源,因其分辨率高、重復性好,被越來越廣泛使用[5]。本研究對杭州地區一起食物暴露不明確的李斯特菌病散發事件的臨床分離株,和流行病學無關聯但具有相同PFGE型別的食品分離株進行了基因組測序,分析基因組序列差異。并與NCBI Assembly公共數據庫中相同多位點序列分型(Multi-locus Sequence Typing, MLST)型別的菌株進行基因組SNPs位點進化分析,研究可能的污染食品溯源與傳播途徑。
1 材料與方法
1.1實驗與分析菌株 選擇PFGEApaI和AscI酶切圖譜完全一致(見圖1)的杭州地區2007-2011年單核細胞增生李斯特菌食品分離株6株和2012年臨床分離株1株(王某,女,22y,中孕,胎死宮內,高熱入院,B超宮內死胎,分離自血培養需氧厭氧雙瓶培養瓶)。多位點序列分型(Multi-locus sequence typing, MLST)結果均為ST8型,菌株背景信息參見表1。對NCBI Assembly公共數據庫中613株單核細胞增生李斯特菌基因組進行MLST分析,獲得ST8型的基因組。
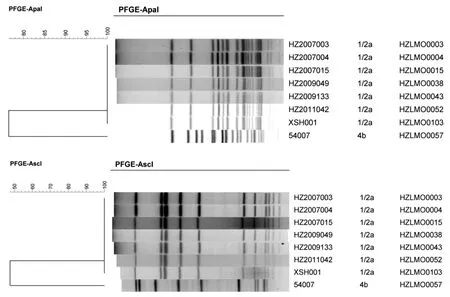
圖1 7株杭州本地食品與臨床來源ST8型單核細胞增生李斯特菌PFGE分型圖譜,CMCC 54007為參考菌株Fig.1 Seven local food and clinical isolates of ST8 type of Listeria monocytogenes PFGE cluster, CMCC 54007 was the reference strain
1.2DNA提取、基因組測序、質控和組裝 采用QIAamp DNA mini Kit試劑盒(德國Qiagen公司,貨號:51304)提取基因組DNA;采用 Nextera XT DNA文庫構建試劑盒(美國illumina公司,型號:FC-131-1024)進行文庫構建;基因組測序應用illumina Miseq平臺,使用Miseq Reagent Kit v3試劑盒(美國illumina公司,型號:MS-102-3003)。以上操作均按試劑盒說明書進行。對測序reads使用FastQC[6]驗證測序質量,用Trimmomatic[7]去除接頭序列。使用shovill[8]和Spades[9]進行基因組拼接。基因組拼接序列使用Quast[10]驗證質量。
1.3毒力基因、ncRNA鑒定和質粒掃描 基因組測序短序列使用srst2[11],拼接序列使用MLST[12]工具掃描獲得ST型別;用Prokka[13]注釋拼接基因組,使用Infernal[14]以Rfam[15]為數據庫鑒定ncRNAs。VFDB(http://www.mgc.ac.cn/VFs)數據庫中66個單核細胞增生李斯特菌毒力基因做為鑒定數據庫,用blastn掃描基因組毒力基因。對本地菌株的基因組拼接序列提交到NCBI blast進行比對,鑒定是否攜帶已知質粒。
1.4基因組共線性和SNPs分析 用Sibelia[16]將杭州本地臨床分離株12-103基因組分別與杭州地區ST8型食品分離株,以及公共數據庫中2株臨床來源的基因組完成圖的菌株Lm-N1546,IZSAM_Lm_15_17439_A144和1株臨床來源的基因組草圖的菌株LM05-00401進行共線性比對。以LM05-00401為參考基因組,用Harvest[17]比對獲得ST8型全基因組SNPs序列。使用Gubbins[18]去除重組,RAxML[19]構建基于SNPs的最大似然法進化樹(模型采用GTR+G,bootstrap=1 000),使用ggtree[20]繪制進化樹。
2 結 果
2.1基因組測序與公共數據庫菌株 7株杭州地區ST8型單核細胞增生李斯特菌基因組測序數據及拼接結果參見表1。采用mlst掃描后,NCBI Assembly公共數據庫中613個單核細胞增生李斯特菌基因組中可獲得已知ST型別的有600個,其中有41株ST8型單核細胞增生李斯特菌株,提取這41株ST8型菌株在NCBI Biosample數據庫中的背景信息,具體參見表2。
2.2毒力基因、ncRNAs序列和質粒分布 毒力基因進行掃描結果顯示除了Lm-N1546和IZSAM-Lm-15-17439-A144缺失virR基因外,其他ST8型菌株均攜帶毒力基因(表3)。杭州本地菌株中12-103的lmo1136多一個9 bp的重復序列,12-004和12-015的lmo2396少204 bp的片段。杭州地區菌株的ncRNAs分子只有rli48、rli62和rliG在分布上有差異。公共數據庫中的菌株只有LM66和LM71缺少rli31。12-003和12-004未發現攜帶質粒,其余5株攜帶pLmA144(KU513859)質粒。菌株的ncRNAs和質粒差異見表3。
2.3基因組共線性和SNPs分析 杭州地區臨床分離株12-103與6株食品分離株和3株國外臨床分離株大于15 kbp片段的共線性均一致,沒有大片段重組現象(共線性結果參見圖2)。基因組SNPs進化樹結果杭州地區分離株與BCW_3902形成一個的分支。總體上12-103與杭州食品分離株高度近源(進化樹參見圖3),12-004與臨床株12-103的進化上最接近,只有16個SNPs差異,相差最多的是24個SNPs位點的12-015。
表1 杭州地區單核細胞增生李斯特菌分離株及基因組測序結果
Tab.1L.monocytogenesisolates and genome sequencing results in Hangzhou
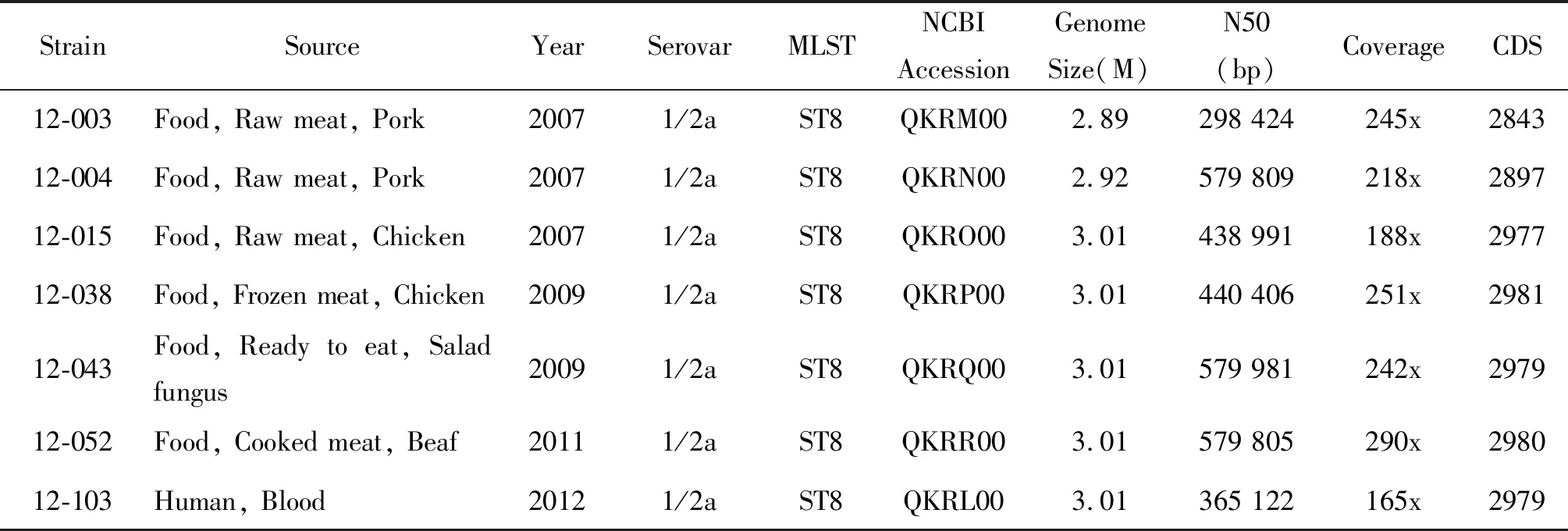
StrainSourceYearSerovarMLSTNCBI AccessionGenomeSize(M)N50(bp)CoverageCDS12-003Food, Raw meat, Pork20071/2aST8QKRM002.89298 424245x284312-004Food, Raw meat, Pork20071/2aST8QKRN002.92579 809218x289712-015Food, Raw meat, Chicken20071/2aST8QKRO003.01438 991188x297712-038Food, Frozen meat, Chicken20091/2aST8QKRP003.01440 406251x298112-043Food, Ready to eat, Salad fungus20091/2aST8QKRQ003.01579 981242x297912-052Food, Cooked meat, Beaf20111/2aST8QKRR003.01579 805290x298012-103Human, Blood20121/2aST8QKRL003.01365 122165x2979
表2 NCBI基因組拼接數據庫中ST8的菌株基因組
Tab.2 Genomes information of ST8 in NCBI assembly database
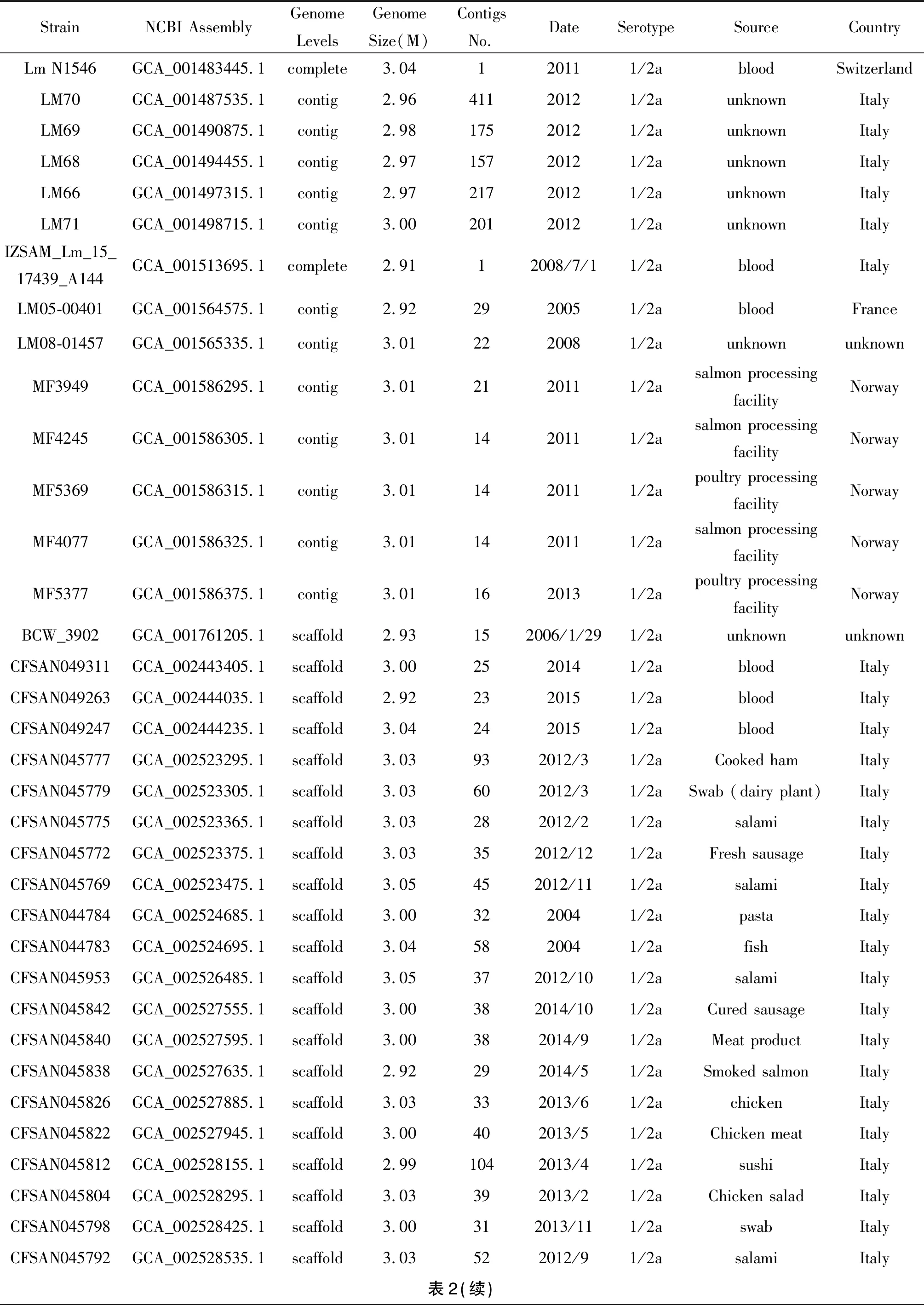
StrainNCBI AssemblyGenome LevelsGenome Size(M)Contigs No.DateSerotypeSourceCountryLm N1546GCA_001483445.1complete3.04120111/2abloodSwitzerlandLM70GCA_001487535.1contig2.9641120121/2aunknownItalyLM69GCA_001490875.1contig2.9817520121/2aunknownItalyLM68GCA_001494455.1contig2.9715720121/2aunknownItalyLM66GCA_001497315.1contig2.9721720121/2aunknownItalyLM71GCA_001498715.1contig3.0020120121/2aunknownItalyIZSAM_Lm_15_17439_A144GCA_001513695.1complete2.9112008/7/11/2abloodItalyLM05-00401GCA_001564575.1contig2.922920051/2abloodFranceLM08-01457GCA_001565335.1contig3.012220081/2aunknownunknownMF3949GCA_001586295.1contig3.012120111/2asalmon processing facilityNorwayMF4245GCA_001586305.1contig3.011420111/2asalmon processing facilityNorwayMF5369GCA_001586315.1contig3.011420111/2apoultry processing facilityNorwayMF4077GCA_001586325.1contig3.011420111/2asalmon processing facilityNorwayMF5377GCA_001586375.1contig3.011620131/2apoultry processing facilityNorwayBCW_3902GCA_001761205.1scaffold2.93152006/1/291/2aunknownunknownCFSAN049311GCA_002443405.1scaffold3.002520141/2abloodItalyCFSAN049263GCA_002444035.1scaffold2.922320151/2abloodItalyCFSAN049247GCA_002444235.1scaffold3.042420151/2abloodItalyCFSAN045777GCA_002523295.1scaffold3.03932012/31/2aCooked hamItalyCFSAN045779GCA_002523305.1scaffold3.03602012/31/2aSwab (dairy plant)ItalyCFSAN045775GCA_002523365.1scaffold3.03282012/21/2asalamiItalyCFSAN045772GCA_002523375.1scaffold3.03352012/121/2aFresh sausageItalyCFSAN045769GCA_002523475.1scaffold3.05452012/111/2asalamiItalyCFSAN044784GCA_002524685.1scaffold3.003220041/2apastaItalyCFSAN044783GCA_002524695.1scaffold3.045820041/2afishItalyCFSAN045953GCA_002526485.1scaffold3.05372012/101/2asalamiItalyCFSAN045842GCA_002527555.1scaffold3.00382014/101/2aCured sausageItalyCFSAN045840GCA_002527595.1scaffold3.00382014/91/2aMeat productItalyCFSAN045838GCA_002527635.1scaffold2.92292014/51/2aSmoked salmonItalyCFSAN045826GCA_002527885.1scaffold3.03332013/61/2achickenItalyCFSAN045822GCA_002527945.1scaffold3.00402013/51/2aChicken meatItalyCFSAN045812GCA_002528155.1scaffold2.991042013/41/2asushiItalyCFSAN045804GCA_002528295.1scaffold3.03392013/21/2aChicken saladItalyCFSAN045798GCA_002528425.1scaffold3.00312013/111/2aswabItalyCFSAN045792GCA_002528535.1scaffold3.03522012/91/2asalamiItaly表2(續)
表3 杭州本地分離株主要毒力基因、non-coding RNA、質粒分布和SNPs位點差異
Tab.3 Distribution of virulence genes, non-coding RNA, plasmid and SNPs differences in local isolates in Hangzhou

isolatelmo1136bplmo2396bpril48ril62133 bp copy130 bp copyrliGplasmidSNPs Numbers12-0031 6292 415-++missND①2312-0041 6292 211③-+-seedND①1612-0151 6292 211③-++fullpLmA144(KU513859)2412-0381 6292 415+--seedpLmA144(KU513859)2012-0431 6292 415-+-seedpLmA144(KU513859)1812-0521 6292 415---seedpLmA144(KU513859)2312-1031 638②2 415+--seedpLmA144(KU513859)/
注:① ND表示未檢測到(Not detected)。
② 多一段9bp重復序列5′-gtagatccg-3′。
③ 缺失一段204bp的序列。
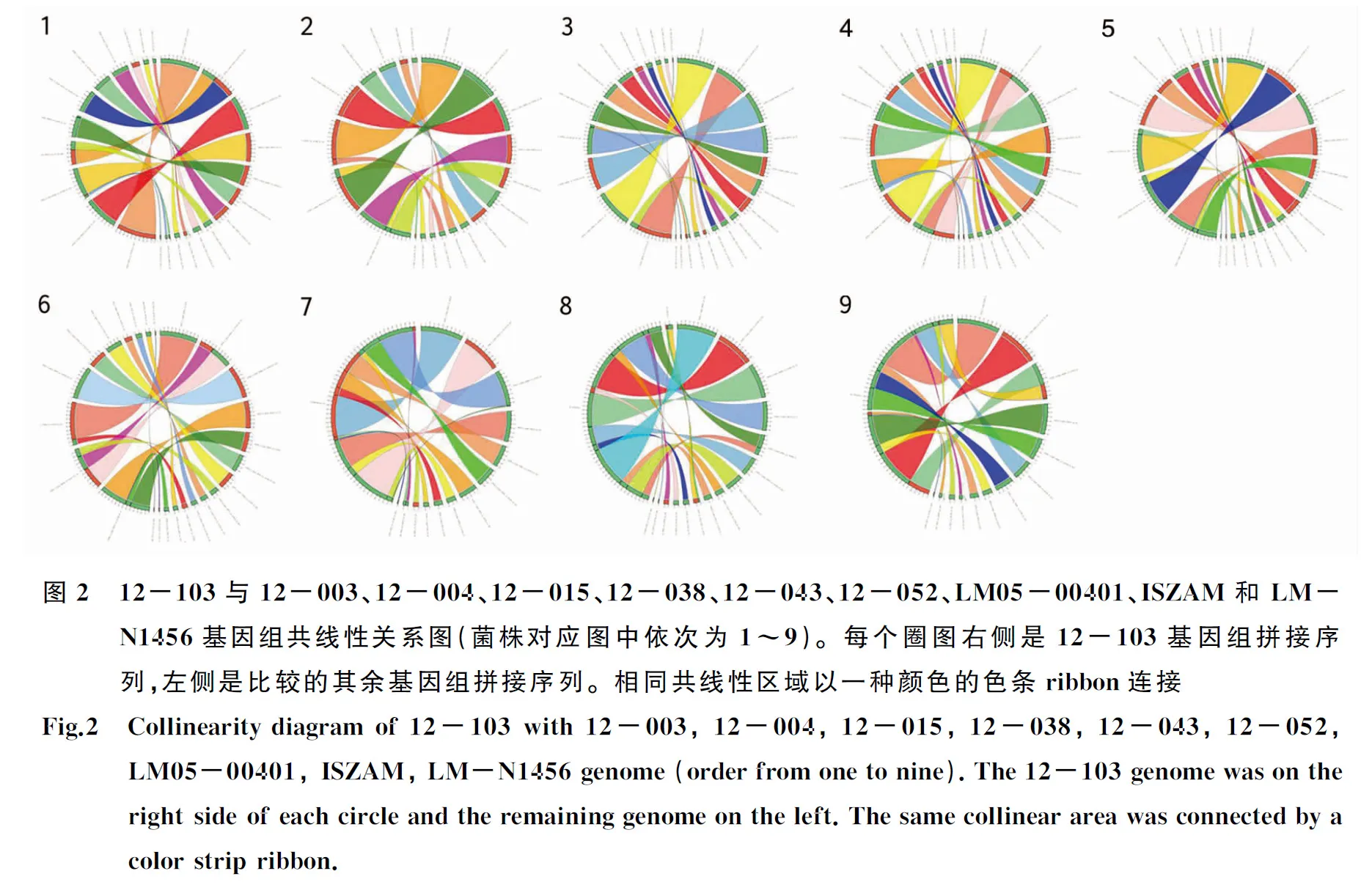
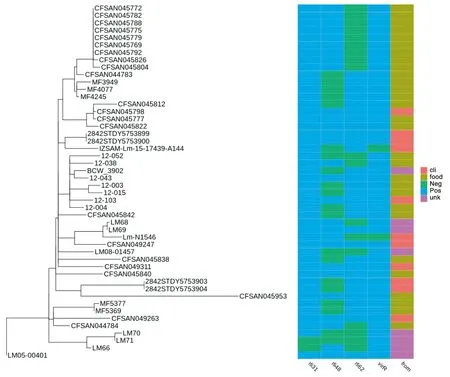
圖3 ST8型單核細胞增生李斯特菌基因組SNPs位點進化樹圖Fig.3 Isolates of L. monocytogenes ST8 genomic SNPs phylogenic tree
3 討 論
單核細胞增生李斯特菌由于其潛伏期長的特點,散發病例難以從流行病學調查攝入食品找到污染病原。缺乏流行病學證據,可以通過病原細菌溯源“金標準” —— PFGE分子分型的方法,以實驗室證據給現場流行病學提供判定依據。但對于一些細菌的特定亞型,PFGE、MLVA等傳統的分子分型技術存在分辨效果不夠的問題。對于杭州地區具有相同PFGE型別的臨床分離株與食品分離株要進行溯源分析,則應采用如高通量測序技術這種精度更高的方法,從基因組層面獲得更為全面準確的信息。
研究表明ST8型菌株主要在肉制品或中間加工過程中分離率較高,具有較強的致病潛力,是一類高度克隆化的型別[21]。PFGE帶型相同的食品分離株均來自不同年份不同地區的生禽、生畜肉,可能這類菌株對肉制品加工流程的環境適應性比較強。對于共線性結果表明12-103與其他杭州食品分離株和國外臨床分離株在基因組層面沒有出現大片段的重組或丟失等現象,這也與杭州地區的菌株PFGE結果帶型一致相符。對于基因組contigs序列排列是否與國外臨床株一致,還需要通過進一步實驗驗證。單核細胞增生李斯特菌毒力基因攜帶率很高[22],毒力調控因子virR基因起重要的調控作用,但2株臨床分離株(Lm-N1546和IZSAM-Lm-15-17439-A144)卻缺失該調控因子。有實驗表明缺失virR基因會明顯降低菌株的耐藥性[23]。本研究中不同來源的ST8型菌株毒力基因分布相同,但部分基因序列結構存在差別。與致死pH值環境中的菌株酸耐受相關[24-25]的lmo0036基因序列中臨床分離株12-103比其他食品分離株序列多了9 bp的富亮氨酸重復(Leucine-rich repeat)序列(gtagatccg)。lmo2396基因是internalin內化素基因,與單核細胞增生李斯特菌靶細胞識別有關[26]。食品分離株12-004和12-015此基因缺失了一個204 bp的區域。ncRNA作為一種在轉錄階段調控整個生物體表達的RNA小分子,其快速調控的特點與細菌環境適應,致病性以及針對宿主免疫應答逃逸功能相關[27]。通過對本地ST8型菌株ncRNA分布掃描,結果表明ncRNAs分布高度一致,只在調控功能與細菌基因水平轉移相關的rli48, rli62和rliG這3個A118 prophage類區域序列[28]位點上有差異。這些序列的差異在臨床株與食品株,以及食品株之間無明顯內在規律。
比較單核細胞增生李斯特菌PFGE和基因組分析的結果,基于參考基因組的ST8型菌株進化關系表明,杭州地區2007-2011年食品分離株與2012年臨床分離株基因組SNPs差異在16~24個之間,基因組核心序列在進化上高度同源。結合國外分離株的基因組,顯示ST8型核心基因組序列高度保守,因此提示PFGE方法可能不適合應用于該型別的分型和溯源。雖然ST8型菌株也存在一些ncRNAs分子和質粒分布上的分子差異,這些差異與致病性相關需要后續進一步進行研究。
本文針對一例臨床散發單核細胞增生李斯特菌分離株與PFGE帶型相同的食品分離株進行基因組序列分析,判斷溯源關系。結果表明杭州市場近年肉類食品中存在遺傳進化高度相似的一群ST8型單核細胞增生李斯特菌,杭州孕婦的感染非常可能來自這群菌株,因此肉制品中ST8型單核細胞增生李斯特菌引起李斯特菌病的安全風險應引起關注。
利益沖突:無

